Tema 2: Data-matricer og Dimensionsreduktion#
I dette tema-projekt skal vi arbejde med “data”-matricer i NumPy og en metode der hedder Principal Component Analysis (PCA). Principal Component Analysis (PCA) er en matematisk (statistisk) metode, der bruges til at reducere dimensionen af data. Metoden prøver at identificere de vigtigste variationer i et datasæt ved at omdanne de oprindelige variabler til nye, uafhængige “komponenter”. I “Matematik 1b-sprog” finder vi en ny ortonormal basis, udvælger de vigtigste basis-retninger og projicerer dataene ned på underrummet udspændt af disse basis-vektorer. Dette gør det lettere at visualisere og analysere kompliceret data. PCA er især nyttig, når man arbejder med store datamængder med mange variable men hvor den essentielle information i dataet kan beskrives med få variable, da det kan hjælpe med at identificere de mest relevante egenskaber og reducere “støj” i data.
Før vi kan kigge på metoden, skal vi først lære at lave matrix-operationer i NumPy – det opfører sig nemlig anderledes end SymPy. NumPy (Numerical Python) er en Python-pakke, der gør det nemt at arbejde med numeriske data. Det er uundværligt for ingeniørstuderende, da det giver effektive værktøjer til matematik, statistik og dataanalyse. Den kan blive nyttig i gruppeprojektet senere i kurset, og vi introducere den derfor i denne tema-øvelse. NumPy indeholder en central datastruktur kaldet “array”, som er en n-dimensionel “container” til tal. Vi vil opfatte disse arrays som matricer og vektorer.
Med “data-matricer” forstår vi blot matricer med decimaltal (dvs. numeriske matricer), der ofte repræsenterer fysiske størrelser, fx en \(n \times 2\) matrix \(X\) med to søjler der angiver hhv. højde og vægt af \(n\) forsøgspersoner. Det er ikke formålet med opgaven at vi skal udlede PCA-metoden eller forstå den fra et statistisk perspektiv. Vi vil derimod anvende den til at “forstå” vores data og illustrere koncepterne egenvektor-basis og ortogonale projektioner for datasæt.
Tema-øvelsen er opbygget af følgende trin:
Matrix-regning i SymPy, NumPy og Maple
Import af datasæt og visualiseringer
PCA af datasæt i 2D
Lav dit eget datasæt i højere dimensioner
Matrix-operationer i computer software#
Vi kigger først på forskellige matrix-operationer i SymPy, NumPy og Maple for matricer og vektorer af små størrelser. Nogle af matrix operationerne kender vi fra matematikken, fx matrix-matrix multiplikation, matrix addition, osv. men andre (især i NumPy) er helt nye. Man kan hurtigt komme til at lave noget i NumPy som ikke giver mening, og det er derfor en god ide at kontrollere sin kode for små eksempler, hvor man kan tjekke udregningerne i hånden.
from sympy import Matrix, init_printing
import numpy as np
import matplotlib.pyplot as plt
init_printing()
Du skal først definere \(A \in \mathbb{R}^{3 \times 3}\) og \(\pmb{x} \in \mathbb{R}^{3 \times 1}\) i de 3 programmer. SymPy og NumPy kan du bruge i samme notebook; Maple-koden må du copy-paste til Maple:
Hvis I ikke har Maple installeret eller aldrig har brugt Maple, så behøver du ikke lave udregningen i Maple.
I SymPy:
A = Matrix([[1, 2, 3], [4, 5, 6], [7, 8, 9]])
x = Matrix([1, 2, 3])
A , x
I NumPy:
A_np = np.array(A, dtype=float) # array bruges i NumPy til at lave matricer
x_np = np.array([1, 2, 3], dtype=float)
A_np, x_np
(array([[1., 2., 3.],
[4., 5., 6.],
[7., 8., 9.]]),
array([1., 2., 3.]))
I Maple (worksheet mode):
> with(LinearAlgebra):
> A := Matrix([[1, 2, 3], [4, 5, 6], [7, 8, 9]]);
> x := Transpose(Matrix([1, 2, 3]));
Spørgsmål a#
Udfør matrix-vektor multiplikationen \(A\pmb{x}\) i SymPy, NumPy og Maple. Matrix-vektor og derfor matrix-matrix multiplikation udføres med forskellig syntax i alle tre programmer, men er enten * (asterisk), . (punktum) eller @ (snabel-a)
Spørgsmål b#
Udtrykket \(A + 2\) har ingen matematisk definition – det giver altså ikke mening matematisk. Undersøg om det giver mening i SymPy, NumPy og Maple, eller om man får en fejl.
Igen opfører alle tre programmer SymPy, NumPy og Maple sig forskelligt. Diskuter hvilket program I synes opfører sig mest hensigtsmæssigt.
Spørgsmål c#
NumPy opfører sig ofte ligesom SymPy (og Maple), fx mht transponering:
A.T, A_np.T
(Matrix([
[1, 4, 7],
[2, 5, 8],
[3, 6, 9]]),
array([[1., 4., 7.],
[2., 5., 8.],
[3., 6., 9.]]))
men NumPy kan lave mange andre smarte manipulationer med arrays. Det betyder også man skal passe ikke at lave fejl. Vigtigt er det at vide at NumPy ikke kender forskel på række- og søjle-vektorer: alle vektorer i NumPy er 1-dimensionale. Man derfor ikke sige om det er en vektor der “står op” eller “ligger ned”, og det har derfor ingen effekt at transponere en vektor i NumPy. Dette kan ses ved at x_np er af størrelsen “3”, ikke “(3,1)” eller “(1,3)”:
A_np.shape, x_np.shape
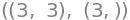
I det følgende skal du forklare hvordan/hvad NumPy udregner, og hvordan du ville opskrive det matematisk eller i SymPy (hvis det overhovedet er muligt):
x_np @ x_np, x_np.dot(x_np)

A_np.dot(x_np)
array([14., 32., 50.])
x_np @ A_np
array([30., 36., 42.])
A_np * x_np, x_np * A_np
(array([[ 1., 4., 9.],
[ 4., 10., 18.],
[ 7., 16., 27.]]),
array([[ 1., 4., 9.],
[ 4., 10., 18.],
[ 7., 16., 27.]]))
Spørgsmål d#
Når vi laver ortogonale projektioner på linjer som i uge 3, har vi ofte brug for at danne en \(n \times n\) projektionsmatrix ud fra matrix-matrix produktet af en \(n \times 1\) søjlevektor og en \(1 \times n\) rækkevektor. I SymPy ville vi gøre:
u = x / x.norm()
u * u.T
_.evalf() # som decimaltal
Hvordan ville du gøre dette i NumPy? Hvorfor virker følgende ikke?
u_np = x_np / np.linalg.norm(x_np)
u_np @ u_np.T
Hint
Vektorer er 1-dimensionale arrays i NumPy så transponering har ingen effekt. Man kan bruge .reshape(n,m) tage at lave disse arrays om til en “to-dimensionale” matricer.
Hint
Fx u_np.reshape(3, 1) og u_np.reshape(1, 3). Mere generelt kan man bruge .reshape(-1, 1) og .reshape(1, -1), hvor vi skrive -1 i stedet for længden af vektoren.
Import af Datasæt og Visualiseringer#
Spørgsmål e#
Download filen weight-height.csv. Data-filen er fra Kaggle og kan også downloads der. Importer CSV-filen i NumPy ved følgende kommando
# Load the CSV file into a NumPy array
data = np.genfromtxt('weight-height.csv', delimiter=',', dtype=[('Gender', 'U10'), ('Height', float), ('Weight', float)], names=True)
# Access the columns by their names
gender = data['Gender']
height = data['Height']
weight = data['Weight']
# Print the data
# print(data.dtype)
print(gender)
print(height)
print(weight)
['"Male"' '"Male"' '"Male"' ... '"Female"' '"Female"' '"Female"']
[73.84701702 68.78190405 74.11010539 ... 63.86799221 69.03424313
61.94424588]
[241.89356318 162.31047252 212.74085556 ... 128.47531878 163.85246135
113.64910268]
Spørgsmål f#
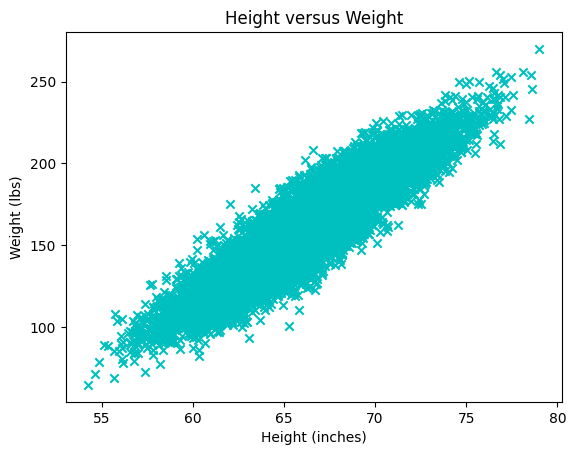
Forklar følgende plot. Hvad svarer hver punkt/kryds til?
plt.scatter(x=height, y=weight, color='c', marker='x')
plt.title("Height versus Weight")
plt.xlabel("Height (inches)")
plt.ylabel("Weight (lbs)")
plt.plot()

Spørgsmål g#
Forklar hvad følgende data-matrix indeholder:
X = np.array([height, weight]).T
X.shape

# de 10 første rækker
X[0:10,:] # eller blot X[:10]
array([[ 73.84701702, 241.89356318],
[ 68.78190405, 162.31047252],
[ 74.11010539, 212.74085556],
[ 71.7309784 , 220.0424703 ],
[ 69.88179586, 206.34980062],
[ 67.25301569, 152.21215576],
[ 68.78508125, 183.9278886 ],
[ 68.34851551, 167.97111049],
[ 67.01894966, 175.9294404 ],
[ 63.45649398, 156.39967639]])
Spørgsmål h#
Skriv en Python funktion der udregner gennemsnit af hver søjle i \(X\)-matricen:
def average_of_each_column(X):
# add code
return X[0,:] # fix this to return the average of each column
Output (efter return) skal være et NumPy array med shape (2,), altså en middelværdi-vektor af længde 2. Tjek din funktion med kaldet:
X - average_of_each_column(X)
Hint
Det letteste er at bruge en indbygget metode. Se https://numpy.org/doc/stable/reference/generated/numpy.mean.html
Spørgsmål i#
Vi skal nu standardisere dataet, hvilket i denne opgave blot består i at centrere punktængden (“data-skyen”) i \((0,0)\). Mere præcist: I hver søjle af \(X\) skal fra hvert element i søjlen fratrækkes søjlens gennemsnit. I Python blot:
def centered(X):
return X - average_of_each_column(X) # 'broadcasting' the vector as we saw above
X_st = centered(X)
Plot det nye standardiserede datasæt \(X_{st}\) og tjek at det er centreret omkring \((0,0)\).
Hint: Husk at datasættet \(X\) kan plottes ved:
plt.scatter(X[:,0], X[:,1]) # X[:,0] er højde og X[:,1] er vægt
plt.title("Height versus Weight")
plt.xlabel("Height (inches)")
plt.ylabel("Weight (lbs)")
plt.plot()

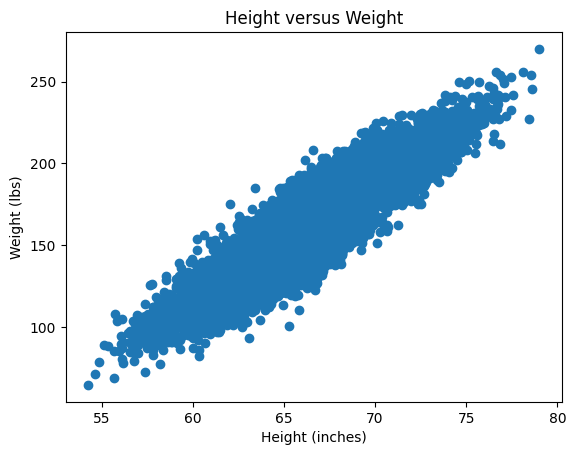
Du skal blot gøre det samme for \(X_{st}\).
Kovariansmatrix#
Spørgsmål j#
Vi vender lige tilbage til matematikken for en kort stund og beder jer bevise følgende:
Lad \(X\) være en vilkårlig reel \(n \times k\)-matrix. Bevis at \(k \times k\)-matricen \(C\) givet ved \(C = X^T X\) er symmetrisk. Argumenter for at \(C\) har reelle egenværdier og \(k\) ortogonale egenvektorer.
Spørgsmål k (valgfri)#
Bevis at \(C\) er faktisk er positive semi-definit og derfor ikke kan have negative egenværdier. Spring gerne denne opgave over og vend tilbage til den senere.
Spørgsmål l#
Vi vender tilbage til den standardiserede data-matrix \(X_{st}\) og udregner \(C\)-matricen ved:
C = 1/(X_st.shape[0]-1) * X_st.T @ X_st
C
array([[ 14.80347264, 114.24265645],
[ 114.24265645, 1030.95185544]])
Matricen \(C\) hedder (sample) kovarians-matricen. Konstanten 1/(X_st.shape[0]-1), der er \(1/(n-1)\), er ikke vigtig for os. Men vi er interesseret i \(C\)s egenværdier og egenvektorer, som findes ved kaldet:
lamda, Q = np.linalg.eig(C)
lamda, Q
(array([ 2.11786479, 1043.63746329]),
array([[-0.99389139, -0.1103626 ],
[ 0.1103626 , -0.99389139]]))
Vis at \(Q\) allerede har normaliserede søjler. Heraf følger at \(Q\) er reel ortogonal. Hvorfor?
PCA og ortogonale projektioner af data#
Spørgsmål m#
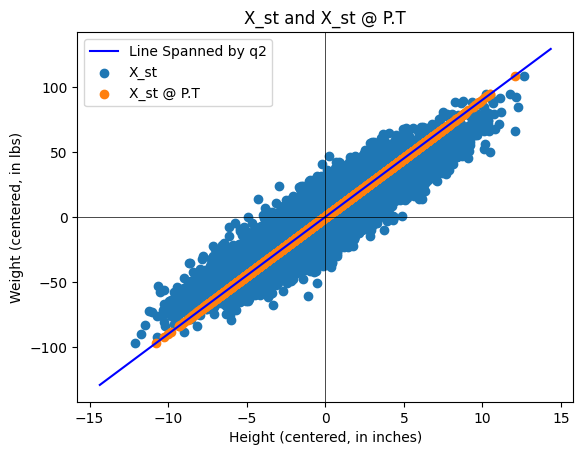
Lav en \(2 \times 2\) projektionsmatrix \(P\) der beskriver den ortogonale projektion ned på egenvektorrummet hørende til den største egenværdi for \(C\). Lad \(\pmb{x}_k\) være den \(k\)’te række i \(X_{st}\), altså vægten og højden af den \(k\)’te forsøgsperson. Som søjlevektor skrives det \((\pmb{x}_k)^T\), som vi kan projicere ned på egenvektorrummet hørende til den største egenværdi ved \(P (\pmb{x}_k)^T\). Hvis vi vil gøre dette for alle forsøgspersoner, skal vi derfor blot udregne \(P (X_{st})^T\). Matricen \(X_{st}\) er af størrelsen \(n \times 2\), mens \(P (X_{st})^T\) er \(2 \times n\) så vi transponere dette for at få samme størrelse som \(X_{st}\), samlet \((P (X_{st})^T)^T = X_{st} P^T\).
Lav først \(P\) matricen. Husk at du udtrækker fx den anden søjle af \(Q\) ved q2 = Q[:,1]. Tjek at \(P\) er en \(2\times 2\) projektionsmatrix.
Plot derefter det standardiserede datasæt \(X_{st}\) sammen med det projicerede datasæt \(X_{st} P^T\). Du skal få et plot der ser ud som:
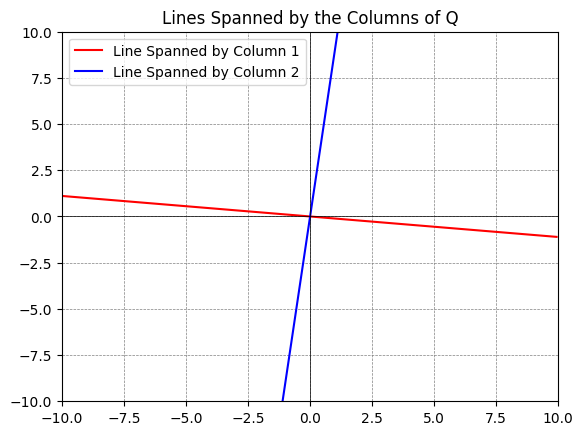
Om Python-plot: Du kan plotte underrum udspændt af søjler i en matrix ved hjælp af følgende kode:
q1 = Q[:,0] # den første søjle
q2 = Q[:,1] # den anden søjle
# Define a range for t, which will be used to extend the lines
t = np.linspace(-10, 10, 2)
# Plotting
fig, ax = plt.subplots()
# For each vector, plot a line that it spans
ax.plot(t*q1[0], t*q1[1], 'r', label='Line Spanned by Column 1')
ax.plot(t*q2[0], t*q2[1], 'b', label='Line Spanned by Column 2')
# Adjust the plot limits and style
plt.xlim(-10, 10)
plt.ylim(-10, 10)
plt.axhline(0, color='black',linewidth=0.5)
plt.axvline(0, color='black',linewidth=0.5)
plt.grid(color = 'gray', linestyle = '--', linewidth = 0.5)
plt.legend()
plt.title('Lines Spanned by the Columns of Q')
# Display the plot
plt.show()
Vores datasæt \(X\) (og \(X_{st}\)) har to komponenter, nemlig 2 egenværdier/egenvektorer. Ved projektionen \(X_{st} P^T\) udfører vi en dimensionsreduktion (fra 2 til 1) ned på den vigtigste dimension af datasættet. I dette eksempel er det ikke fornuftigt at lave denne dimensionsreduktion, da både variansen i vægt og højde er vigtig, men vi har lavet den bedste repræsentation hvis vi kun har en “komponent/koordinatvektor”.
Hvis dataet \(X_{st}\) havde \(k\) søjler og \(C\)-matricen derfor blev \(k \times k\) med \(k\) egenværdier, bør man lave ortogonal projektion af \(X_{st}\) ned på underrummet af \(\mathbb{R}^k\) udspændt af egenvektorerne hørende til de “største” egenværdier, da dette er de “vigtigste” komponenter. Hvis egenværdierne for \(C\) fx er \(1,0.7,0.5,0.01,001\), bør \(P\) lave den ortogonale projektion på underrummet udspændt af egenvektorerne hørende til de tre største egenværdier.
Spørgsmål n#
I stedet for at se på projektionen i det oprindelige 2D-rum (som i forrige spørgsmål), kan vi finde punktets koordinat (placering) på selve egenvektor-aksen hørende til den vigtigste komponent. Dette gøres ved \(Z=X_{st}\pmb{q}_{2}\). Forklar hvorfor vi vælger \(\pmb{q}_2\)-vektoren. Forklar hvilken dimension \(Z\) har, og hvorfor dette kaldes dimensionsreduktion. \(Z\) kaldes normalt PCA scores.
Spørgsmål o#
Lad os kigge på nogle datamatricer \(Y\) med 3 søjler så vi kan opfatte \(Y\) som en punktmængde i \(\mathbb{R}^3\). Datamatricen \(Y\) i koden nedenfor genereres “tilfældigt”, men efter reglerne:
\(Y\) er standardiseret (hver søjle har nul som gennemsnit),
Egenværdierne for \(C= \frac{1}{n-1} Y^T Y\) er omtrentlig lig med \(\lambda_1, \lambda_2. \lambda_3\), som angives af brugeren i linjen
eigenvalues = [5, 1, 0.04].
# Function to generate a synthetic dataset
def generate_3d_data(eigenvalues, size=1000, dim=3):
# Eigenvalues specified by the user
assert len(eigenvalues) == dim, "There must be exactly dim eigenvalues."
# Create a diagonal matrix for the eigenvalues
Lambda = np.diag(eigenvalues)
# Generate a random orthogonal matrix (eigenvectors)
Q, _ = np.linalg.qr(np.random.randn(dim, dim))
# Generate random data from a standard normal distribution
data_standard_normal = np.random.randn(size, dim)
# Transform the data using the square root of the covariance matrix
data_transformed = data_standard_normal @ np.sqrt(Lambda) @ Q.T
# Construct the covariance matrix
Cov = 1/(size-1) * data_transformed.T @ data_transformed
return data_transformed, Cov
# Eigenvalues you want for your covariance matrix
eigenvalues = [5, 1, 0.04]
# Generate the data
Y, C = generate_3d_data(eigenvalues)
Vi kan plotte data-matricen \(Y \in \mathbb{R}^{1000 \times 3}\) som 1000 datapunkter i \(\mathbb{R}^3\):
# %matplotlib qt # plottes i et nyt vindue som kan roteres, fjern #
fig = plt.figure()
ax = fig.add_subplot(111, projection='3d')
ax.scatter(Y[:,0], Y[:,1], Y[:,2], c='b', marker='x')
ax.set_xlabel('first column')
ax.set_ylabel('second column')
ax.set_zlabel('third column')
plt.title('3D Scatter Plot of Synthetic Data')
plt.show()

Vælg forskellige positive \(\lambda_1, \lambda_2, \lambda_3\) i eigenvalues = [5, 1, 0.04] og undersøg den fremkomne punktmængde ved at rotere plottet (du skal udkommentere %matplotlib qt). Prøv både med eksempler hvor \(\lambda_1\) er meget større end \(\lambda_2, \lambda_3\), og hvor \(\lambda_3\) er meget mindre end \(\lambda_1\) og \(\lambda_2\). Hvordan ændrer punktmængdens form sig med egenværdierne?
Tænkt på dette (løst formulerede udsagn): Egenværdierne i \(C\) er løst sagt givet ved semi-akserne i den ellipsoide der bedst kan “dække” de fleste datapunkter. Retningen på ellipsoidens symmetri-akser bestemmes af egenvektorerne. Ikke vigtige “komponenter” er i retninger, hvor ellipsoiden er “flad”.
Svar
En stor \(\lambda_1\) og små \(\lambda_2, \lambda_3\): Dataskyen bliver til en langstrakt “cigar” eller nål langs \(\pmb{q}_{1}\)-aksen.
\(\lambda_1 \approx \lambda_2\) store og \(\lambda_3\) lille: Dataskyen bliver flad som en “pandekage” i planen udspændt af \(\pmb{q}_{1}\) og \(\pmb{q}_{2}\).
\(\lambda_1, \lambda_2, \lambda_3\) alle af samme størrelse: Dataskyen bliver en kugleformet sky uden nogen dominerende retning.
Spørgsmål p#
I denne tema-øvelse centrerer vi datasættet ved at trække middelværdien fra hver søjle. Det kan også være nyttigt (eller nødvendigt) at “skalere” dataene, så alle søjler får samme spredning (dvs. at variationen i hver søjle bliver ens). Denne standardisering kaldes samlet z-score normalisering, hvor dataene transformeres, så hver søjle får middelværdi 0 og spredning 1.
Diskuter hvornår kan det være nødvendigt at standardisere dataene på denne måde (inden kovariansmatricen udregnes og PCA udføres)?
Hint
Overvej følgende punkter i din diskussion:
Når variablerne måles i forskellige enheder (fx centimeter vs. kilo), kan de med større “enheder” dominere kovariansmålingerne.
Hvis du har en variabel målt i millimeter og en i kilometer, vil millimeter-variablen have en numerisk meget større varians, selvom den måske er mindre vigtig.
Hvis variablerne har meget forskellige spredninger, kan variablen med størst variation komme til at bestemme de fundne hovedkomponenter, selvom den måske ikke er den vigtigste for problemstillingen.
Ved at anvende z-score normalisering sikres det, at alle variabler bidrager ligeligt til analysen, da de nu alle har samme mål for spredning.
Diskuter også, om der kan opstå situationer, hvor det ikke er hensigtsmæssigt at skalere dataene, fx hvis den absolutte varians i variablerne er en vigtig del af fortolkningen af dataene.
Svar
Nødvendigt: Når enhederne er forskellige (fx indkomst i kr. vs. alder i år). Ellers vil PCA blot pege på den variabel med de største talværdier.
Ikke nødvendigt: Hvis alle variabler er i samme enhed (f.eks. pixels i et billede eller centimeter i biologiske mål), og den relative forskel i spredning faktisk bærer vigtig information.
Ekstra Frivillig Opgave: PCA på Iris-datasættet (4D)#
I denne afsluttende (frivillige) del skal vi arbejde med det berømte Iris-datasæt. Datasættet indeholder 150 observationer af tre forskellige arter af iris-blomster (Setosa, Versicolor og Virginica). Hver blomst er beskrevet ved 4 fysiske målinger (features): bægerblads-længde/bredde og kronblads-længde/bredde.
Formålet med denne del er at undersøge, om de fire fysiske målinger (længde og bredde af bæger- og kronblade) er tilstrækkelige til at skelne mellem de tre forskellige arter af Iris-blomster. Da vi ikke kan visualisere fire dimensioner på én gang, bruger vi PCA som en “matematisk projektor” til at transformere dataene.
Vi ønsker at se, om blomsterne naturligt optræder som tre adskilte grupper (klynger). Hvis arterne samler sig i hver deres gruppe, beviser det, at de fysiske forskelle er systematiske nok til, at vi kan klassificere blomsterne matematisk.
Først skal vi indlæse data. Hvis du ikke har scikit-learn installeret, kan det gøres i terminalen med conda install scikit-learn.
from sklearn.datasets import load_iris
import matplotlib.pyplot as plt
import numpy as np
iris = load_iris()
X_iris = iris.data # 150x4 matrix (målinger)
y_iris = iris.target # Vektor med arter (0, 1 eller 2)
names = iris.target_names
Spørgsmål q: Visualisering af rådata i 3D#
Da vi lever i en tredimensionel verden, kan vi ikke visualisere alle 4 koordinater på én gang. Vi starter derfor med at “smide” en koordinat væk og plotte de første tre målinger direkte.
Brug følgende kode til at se på data i \(\mathbb{R}^{3}\):
# %matplotlib qt
fig = plt.figure(figsize=(8, 6))
ax = fig.add_subplot(111, projection='3d')
# Vi vælger de første 3 ud af 4 søjler til x, y og z akserne
colors = ['r', 'g', 'b']
for i in range(3):
ax.scatter(X_iris[y_iris == i, 0],
X_iris[y_iris == i, 1],
X_iris[y_iris == i, 2],
c=colors[i], label=names[i])
ax.set_xlabel(iris.feature_names[0])
ax.set_ylabel(iris.feature_names[1])
ax.set_zlabel(iris.feature_names[2])
ax.set_title("Direkte målinger i 3D")
ax.legend()
plt.show()
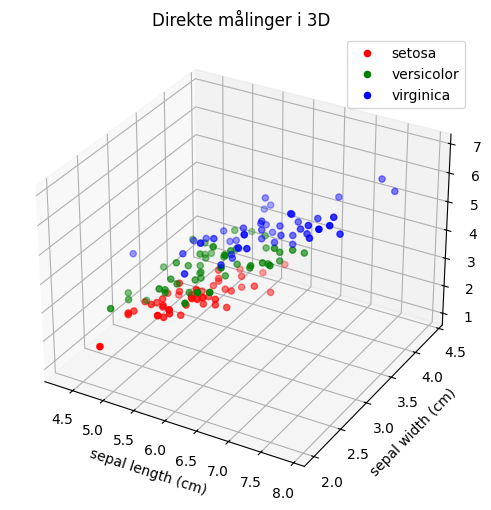
Er det nemt at adskille de tre arter fra hinanden baseret på disse projektioner af direkte målinger? Hvad mister vi ved at fravælge en af de fire målinger? Kan du adskille de tre arter hvis du vælger andre af de direkte features/målinger end de tre første?
Note
Husk at udkommentere %matplotlib qt, hvis du vil kunne rotere 3D-plottet i et separat vindue.
Spørgsmål r: Kovarians og Egenværdier#
For at lave en mere intelligent dimensionsreduktion end blot at slette en søjle, skal vi bruge PCA.
Standardiser data: Træk middelværdien fra hver søjle i \(X_{iris}\) , så data er centreret i origo. Kald resultatet \(X_{st}\).
Beregn kovariansmatricen: Udregn \(C=\frac{1}{n-1}(X_{st})^T X_{st}\), hvor \(n=150\). Hvilken dimension har denne matrix?
Find egenværdier: Beregn de fire egenværdier for \(C\).
Find dominerende egenvektorer: Find de egenvektorer der hører til de tre største egenværdier. Kald disse \(\pmb{q}_{1}, \pmb{q}_{2}, \pmb{q}_3\).
Angiv \(\pmb{q}_{1}, \pmb{q}_{2}\) og \(\pmb{q}_3\).
Spørgsmål s: Fra 4D til 3D via hovedkomponenter#
Vi vil nu projicere data ned i 3D ved hjælp af de tre vigtigste hovedkomponenter (PCA-retningerne \(\pmb{q}_{1}, \pmb{q}_{2}, \pmb{q}_{3}\), svarende til de tre største egenværdier). Vi danner matricen \(Q_{reduced}=\left[\pmb{q}_{1},\pmb{q}_{2}, \pmb{q}_{3}\right]\) af størrelse \(4\times 3\) .
De nye 3D-koordinater (også kaldet PCA scores) beregnes som:
Færdiggør koden og kommenter på resultatet:
Q_reduced = ... # Husk at sortere dem efter de største egenværdier
Z = X_st @ Q_reduced # Projektionen
fig = plt.figure(figsize=(10, 8))
ax = fig.add_subplot(111, projection='3d')
colors = ['r', 'g', 'b']
for i, target_name in enumerate(names):
# Vi bruger de tre søjler i Z som hhv. x, y og z koordinater
ax.scatter(Z[y_iris == i, 0],
Z[y_iris == i, 1],
Z[y_iris == i, 2],
c=colors[i],
label=target_name,
s=50)
ax.set_xlabel('Principal Component 1')
ax.set_ylabel('Principal Component 2')
ax.set_zlabel('Principal Component 3')
ax.set_title('PCA med 3 koordinater')
ax.legend()
plt.show()
Hvad fortæller plottet dig om de tre blomsterarter sammenlignet med 3D-plottet i spørgsmål q? Er det muligt at kende forskel på arterne nu, selvom vi kun bruger 3 dimensioner i stedet for 4?

